Investigadores de la Universidad de Illinois han programado una bacteria digital para que se divida con enorme precisión espacial y temporal
Una célula simulada en las primeras etapas de división. La mitad izquierda muestra el citoplasma (cubos azules), moléculas de la maquinaria de degradación de ARNm (rosa) y transportadores de azúcar (marrón). La mitad derecha añade la membrana (verde) y los ribosomas (amarillo/rojo). De la Figura 1 del artículo, "Bringing the genetically minimal cell to life on a computer in 4D". Revista: Cell. DOI: 10.1016/j.cell.2026.02.009Zane ThornburgEurekalert
Ignacio Crespo
larazon.es/Madrid Creada: 09.03.2026
Desde fuera las células parecen poco trepidantes. Semejan masas gelatinosas que engordan poco a poco hasta que les da por partirse en dos. No parece haber mucho misterio y, desde luego, no parece que debiera llevar años crear una réplica por ordenador. Sin embargo, quien se ha enfrentado al proceloso mundo de la biología celular sabe que, en realidad, el interior de la célula es un verdadero enjambre de moléculas. De hecho, incluso su membrana contiene incontables estructuras que, atrapadas en ellas, sirven de peajes con el medio. Simular cada detalle en la vida de una bacteria podría compararse con simular una ciudad, con sus cientos de miles de habitantes y, ahora, un grupo de científicos de la Universidad de Illinois, lo ha logrado.
Un estudio que acaba de ser publicado en la revista científica Cell muestra las primeras imágenes de la bacteria simulada. Sin cierto contexto podríamos pensar que sus autores han estado jugando demasiado al Minecraft, pero todo parecido se limita a esos diminutos cubos con los que han representado la membrana, el citoplasma que la rellena y los ribosomas que se encargan de convertir el material genético en proteínas (cubos verdes, azules y la combinación de amarillos y rojos respectivamente). La célula elegida es una bacteria que han bautizado como JCVI-syn3A (Syn3A para abreviar) y, por decirlo así, cada “pixel” que la compone es de escala nanométrica. Y, para hacernos una idea: el grosor de un pelo alcanza los 60.000 nanómetros, un virus puede rondar los 30 nanómetros y la hélice de tu ADN apenas tiene 2,5 nanómetros de diámetro.
La simulación ha requerido de años de trabajo hasta alcanzar el nivel de detalle que el equipo buscaba. Desde que empezaron a recopilar los datos experimentales y eligieron qué querían representar hasta que corrieron las últimas simulaciones, la cantidad de datos y decisiones no dejó de crecer. De hecho, el resultado es tan minucioso que, si muestran todas las moléculas simuladas al mismo tiempo, la bacteria se vuelve un borrón impenetrable. Para poder distinguir los procesos que ocurren en su interior tienen que hacer otros invisibles. Y es que los investigadores tuvieron en cuenta cada gen, cada proteína y molécula de ARN, cada reacción química que ocurriera en el interior de la bacteria o en su superficie durante los 105 minutos simulados (eso sí: donde cada proceso ocurría con menos de 2 minutos de diferencia respecto al ciclo celular real).
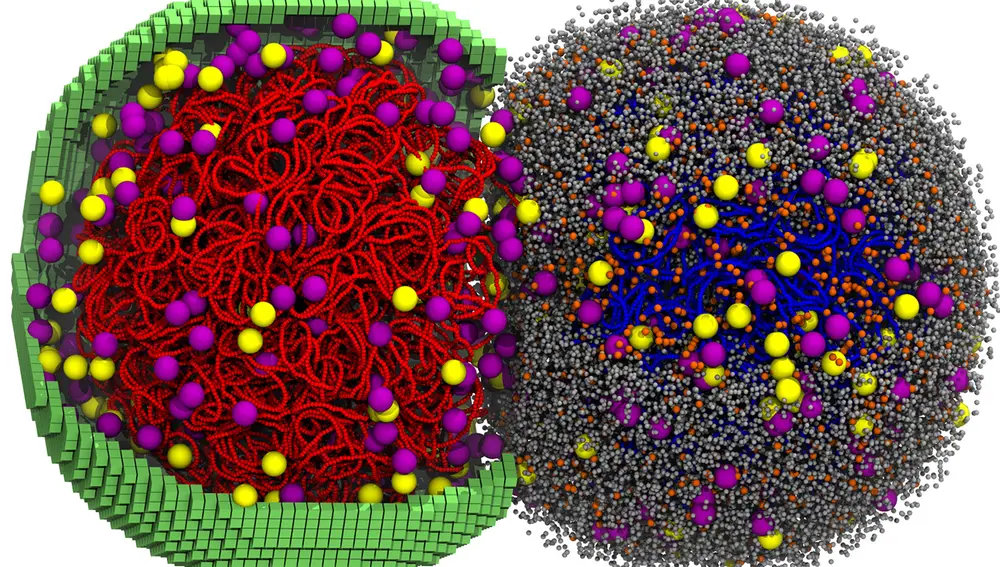
Una célula simulada en las primeras etapas de división. La mitad izquierda muestra la membrana (cubos verdes) y los ribosomas (amarillo/morado) entretejidos a través del cromosoma de la célula (rojo). El lado derecho muestra todas las proteínas (gris) y el ARN (naranja) dentro de la célula con un pequeño corte para mostrar una segunda copia del cromosoma de la célula (azul). De la Figura 1 del artículo, "Bringing the genetically minimal cell to life on a computer in 4D". Revista: Cell. DOI: 10.1016/j.cell.2026.02.009Zane ThornburgEurekalert
Porque, efectivamente, este “filme” solo dura una hora y cuarenta y cinco minutos y ocurre en tiempo real. Dicho de otro modo: no condensa horas de actividad celular. Sin embargo, el tiempo que han necesitado para computar la simulación completa en sus últimas versiones superaba los 6 días. Esto es: cada minuto de película tardaba en procesarse cada una hora y media. Tiempo que era incluso mayor antes de que los investigadores decidieran destinar una unidad de procesamiento gráfico completa (GPU) solo para simular la replicación del ADN. Antes de implementar esta decisión, cada minuto de la simulación tardaba casi 3 horas en ser procesado.
¿Y para qué?
Pero, aparte del interés intelectual que pueda saciar esta simulación… ¿Qué propósito perseguían sus investigadores? ¿Tendrá Syn3A algún impacto en nuestra sociedad o es una nota curiosa al pie de página de nuestro siglo? En realidad, ambas cosas son compatibles y la segunda pregunta es más difícil de responder que la primera. Sí podemos aclarar que, en palabras de Luthey-Schulten: “La capacidad de capturar con precisión las condiciones en constante cambio dentro de una célula viva abre una nueva ventana a los fundamentos de los sistemas vivos. Tenemos un modelo de célula completa que predice muchas propiedades celulares simultáneamente", dijo. "Si quieres saber qué está pasando, por ejemplo, en el metabolismo de nucleótidos, también puedes observar qué está pasando en la replicación del ADN y la biogénesis de los ribosomas. Así que las simulaciones pueden darte los resultados de cientos de experimentos simultáneamente".
Estas simulaciones por ordenador no dejarán obsoleta la investigación tradicional, ni mucho menos, pero servirá de complemento para hacer mejores preguntas y establecer mejores hipótesis de partida. En definitiva: Syn3A (o sus sucesoras) podrían habilitarán nuevas formas de hacer ciencia, más rápidas, más dirigidas y más eficiente.
QUE NO TE LA CUELEN:Aunque solemos imaginar las simulaciones como películas de animación, lo cierto es que suelen ser grandes cantidades de números. Tablas, gráficos y respuestas que no tienen por qué requerir de una célula representada en las tres dimensiones del espacio. La modelización 3D suele ser una opción y en este artículo podemos ver cómo representan la célula, pero más que imágenes, lo que buscan son cifras precisas que les permita diseccionar con gran precisión qué está pasando.
_______________
REFEREMCIAS (MLA):
Thornburg, Zane, et al. "Bringing the Genetically Minimal Cell to Life on a Computer in 4D." Cell, vol. 188, no. 5, 9 Mar. 2026, doi:10.1016/j.cell.2026.02.009.
________
Fuente:




